Oct 31, 2025
Procolo de análisis bioinformático elemental: desde acceso al GenBank al análisis genético
- Dumar Jaramillo-Hernández1,
- lf.salazar 2
- 1Universidad de los Llanos (Colombia);
- 2Universidad Técnica de Ambato (Ecuador)
- Dumar_Jaramillo_H

Protocol Citation: Dumar Jaramillo-Hernández, lf.salazar 2025. Procolo de análisis bioinformático elemental: desde acceso al GenBank al análisis genético. protocols.io https://dx.doi.org/10.17504/protocols.io.kxygx48zwl8j/v1
License: This is an open access protocol distributed under the terms of the Creative Commons Attribution License, which permits unrestricted use, distribution, and reproduction in any medium, provided the original author and source are credited
Protocol status: Working
We use this protocol and it's working
Created: October 29, 2025
Last Modified: October 31, 2025
Protocol Integer ID: 231080
Keywords: Bioinformática, Toxocara, Filogenia, análisis bioinformático básico asociado al ingreso al genbank, al genbank al análisis genético protocolo, genbank to genetic analysis, basic bioinformatics analysis protocol, análisis bioinformático, genetic analysis, proteínas de diversos organismo, genes from microorganism, sequencing gene fragment, genetic distances between genbank repository, distanciamientos genéticos entre, accessing genbank, result of molecular diagnostic product, gene repository, proteins from various organism, gene fragment, genbank repository, molecular diagnostic product, subsequent phylogenetic analysis, microorganism, comparing genetic distance, gene, genbank, procesos elementales para entender principio, various organism, complete genome
Abstract
Protocolo de análisis bioinformático básico asociado al ingreso al GenBank, búsqueda de depósito de genes, fragmentos de genes, genomas completos o proteínas de diversos organismos, posterior prinicipio de análisis filogenético usando secuencias FAST de los depósitos y mecanismos de comparacioes de distanciamientos genéticos entre depósitos del GenBank. Procesos elementales para entender principios de acciones a seguir posterior a la secuenciación de fragmentos génicos o genes de microganismos, como resultado de productos de diagnósticos molecular (ej. PCR convencional).
Basic bioinformatics analysis protocol: from accessing GenBank to genetic analysis
Basic bioinformatics analysis protocol associated with accessing GenBank, searching for gene repositories, gene fragments, complete genomes, or proteins from various organisms, subsequent phylogenetic analysis using FAST sequences from the repositories, and mechanisms for comparing genetic distances between GenBank repositories. Elementary processes for understanding the principles of actions to be taken after sequencing gene fragments or genes from microorganisms, as a result of molecular diagnostic products (e.g., conventional PCR).
Attachments
Guidelines
Otras bases de datos abiertas de depósitos de información génica o proteoma en el mundo que deben ser consultadas
| Base de Datos | Qué contiene | Enlace | |
| NCBI GenBank | Secuencias de ADN, ARN, proteínas | https://www.ncbi.nlm.nih.gov/genbank/ | |
| EMBL-EBI (ENA) | Archivo europeo de secuencias | https://www.ebi.ac.uk/ena | |
| DDBJ (Japón) | Parte del consorcio internacional con NCBI y EMBL | https://www.ddbj.nig.ac.jp/ | |
| UniProt | Secuencias y anotaciones de proteínas | https://www.uniprot.org/ | |
| BOLD Systems | Secuencias de código de barras genético (usado en taxonomía) | https://www.boldsystems.org/ |
Materials
Computador.
Se puede trabajar desde CDM de windows o desde la terminal de Mac.
Acceso a internet.
Troubleshooting
Safety warnings
MrBayes IQ-TREE y BEAST
Importante, si bien son herramientas muy robustas, se necesita tener conocimientos previos de lenguaje de programación, se puede trabajar desde CDM de windows o desde la terminal de Mac
Ethics statement
Son experimentos in-silico, exclusivamente análisis computacionales de información génica o proteoma dispuesta en la web en bases de datos. Dependiendo de los usos que le darán a la información analizada y generada, deberán solicitar avales a los IACUC.
Before start
Programas para alineamiento de secuencias:
Clustal Omega Para alineamientos múltiples. https://www.ebi.ac.uk/Tools/msa/clustalo/
MAFFT Para grandes volúmenes de secuencias. https://mafft.cbrc.jp/alignment/server/
MUSCLE Alineamientos múltiples. https://www.ebi.ac.uk/jdispatcher/msa/muscle?stype=protein
Programas para construir árboles filogenéticos:
- Permite alineamientos, construcción y visualización de árboles.
- Ideal para principiantes
PhyML http://www.atgc-montpellier.fr/phyml/
- Usa métodos de Máxima Verosimilitud para árboles más robustos.
RAxML (Randomized Axelerated Maximum Likelihood) https://evomics.org/learning/phylogenetics/raxml/
- Muy eficiente para grandes conjuntos de datos.
- Basado en máxima verosimilitud.
MrBayes https://sourceforge.net/projects/mrbayes/
- Utiliza inferencia bayesiana para construir árboles con estimaciones probabilísticas.
IQ-TREE https://iqtree.github.io/
Rápido y automatizado, muy usado en filogenias modernas.
BEAST https://beast.community/
- Especializado en análisis filogenéticos con información temporal (ej. evolución viral).
Visualización de árboles filogenéticos:
FigTree http://tree.bio.ed.ac.uk/software/figtree/
- Intuitivo y útil para editar y personalizar árboles.
iTOL (Interactive Tree Of Life) https://itol.embl.de/
- Permite crear árbolesinteractivos, con colores, etiquetas, etc.
Metodología desde el acceso al GenBank al análisis genético
Selecciona qué tipo de información registrada se desea acceder (ej. genes, genoma completo,
proteínas ..) Nota: Cuando es un fragmento de un gen, dejar “All Databases”.
Colocar la búsqueda del gen o proteína requerido “Search”
Nota: Para este caso fue un fragmento del DNA ribosomal del nematodo Toxocara
(ITS-1)
Buscar secuencias depositadas (o nucleóticos, o péptidos, o documentos publicados con ese
fragmento de DNA en Toxocara …) Nota: Para este caso "Nucleotide 55"
Identificar la parte amplificada versus lo depositado en NCBI + Secuencia FASTA
Dirigirse a “Run BLAST”
A. Pegar secuencia FAST + B. Procurar el organismo + C. click “BLAST”
Esperar cargue de información en página nueva e ir a las secuencias depositadas en la parte
inferior de la página
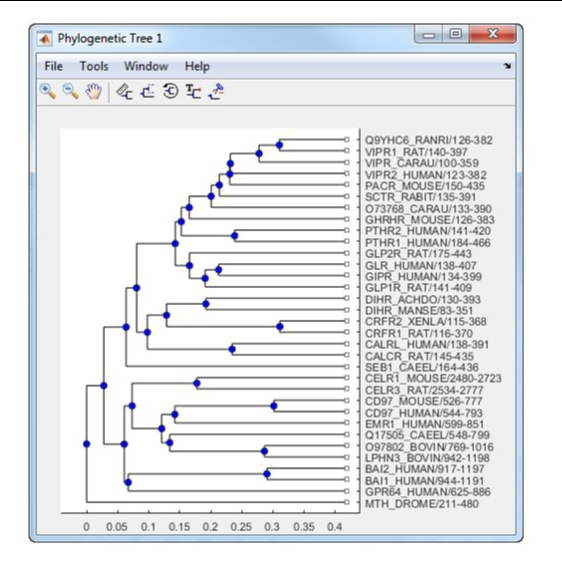
Seleccionar las secuencias para el estudio genético (ej. a través de árboles filogenéticos)
BLAST permite generar estudios filogenéticos a través de distanciamiento génico por arboles, esta
salida del software permite descargarse en varios tipos de archivos, hasta en PDF.
Otra forma de análisis genético: En la página inicial de BLAST (https://blast.ncbi.nlm.nih.gov/Blast.cgi) acceder al “Global Align”
Permite comparar depósitos de secuencias de nucleótidos (Para este caso ITS-2 de T. canis versus T. cati) + Click “BLAST”
Análisis específicos de distanciamiento genético entre dos fragmentos de gen o genes.
Se puede graficar el análisis:
Protocol references
Acknowledgements
A la Dirección General de Investigaciones de la Universidad de los Llanos por proveer los recursos para la estancia corta de investigación del profesor Dumar A. Jaramillo Hernández.

